Nyt AI-værktøj fra DTU skal opdage bakterier før de bliver farlige




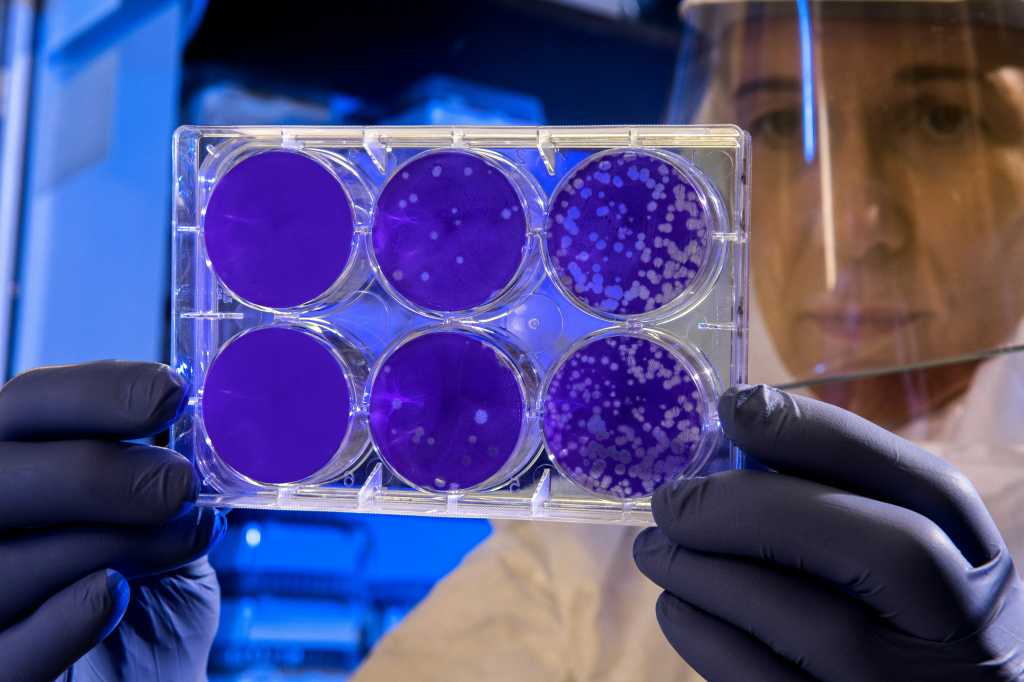
Et nyt AI-baseret værktøj fra DTU Fødevareinstituttet skal gøre det muligt at opdage farlige bakterier, før de udvikler sig til større sundhedskriser. Værktøjet, der hedder PathogenFinder2, analyserer genetiske data for at vurdere, om ukendte bakterier kan være sygdomsfremkaldende.
Ifølge forsker Alfred Ferrer Florensa er målet at kunne identificere trusler, også når der er tale om helt nye bakterier, som man ikke tidligere har set. Værktøjet gennemgår blandt andet prøver fra spildevand, mennesker og dyr for at finde mønstre, der kan indikere risiko.
Metoden bygger på kunstig intelligens, der – ligesom sprogmodeller – lærer at genkende strukturer, i dette tilfælde proteiner i bakterier. På den måde kan systemet forudsige, hvilke bakterier der potentielt kan udgøre en sundhedsrisiko.
PathogenFinder2 er udviklet på baggrund af analyser af over 21.000 bakteriers DNA og er ifølge DTU bedre til at håndtere ukendte bakterier end tidligere modeller. Samtidig kan værktøjet forklare sine vurderinger, hvilket gør det lettere for forskere at arbejde videre med resultaterne.
Forskerne understreger dog, at værktøjets resultater ikke kan stå alene. De identificerede risici skal fortsat undersøges nærmere, før der kan drages endelige konklusioner.
Med det nye værktøj håber DTU at styrke beredskabet mod fremtidige pandemier ved at opdage trusler tidligere end hidtil.
Faktaboks:
- Værktøj: PathogenFinder2
- Udviklet af: DTU Fødevareinstituttet
- Formål: Identificere potentielt sygdomsfremkaldende bakterier
- Metode: Kunstig intelligens analyserer genetiske data
- Datagrundlag: Over 21.000 bakteriers DNA
- Prøver: Spildevand, mennesker og dyr
- Forsker: Alfred Ferrer Florensa
- Styrke: Bedre til at opdage ukendte bakterier end tidligere modeller
- Funktion: Kan forklare sine egne vurderinger
- Forbehold: Resultater kræver yderligere videnskabelig undersøgelse












 Accepter kun nødvendige cookies
Accepter kun nødvendige cookies